概要#
欢迎来到 braincell 的世界!
本节简要介绍了 braincell 框架的一些关键概念及相关建模。
braincell 是一个专为神经元建模设计的高性能计算框架,基于JAX 和 brainstate 构建。它为神经科学研究者、计算神经科学家和类脑计算工程师提供了一套完整的工具链,用于构建、模拟和优化从离子到多尺度神经网络的电生理精确模型,并且整合了现代硬件加速、自动微分等先进特性。以下教程将详细介绍其层次架构和核心功能,帮助你快速理解 braincell 的构建逻辑。
import brainunit as u
import brainpy
import braincell
import brainstate
import matplotlib.pyplot as plt
层级架构#
在神经元建模中,我们通常将模型按照结构复杂度与功能层次,划分为以下几个主要层级:
ChannelIonCell
braincell 用于进行精确的神经元动力学建模,专注于以上三个层级。
Channel:膜上的离子通道,控制特定离子的通透性,决定电流流动。Ion:最基本的带电离子,如 Na⁺、K⁺、Ca²⁺ 等,驱动膜电位变化。Cell:单个神经元的建模单位,用于整合多个通道并产生膜电位变化。
以 HH 神经元为例,其中三者大体的结构如下图:
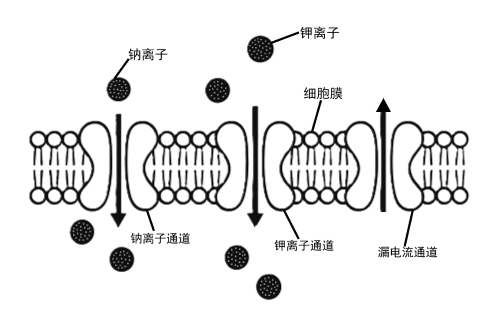
通过这张图不难看出,Channel 、 Ion 、Cell 在结构上有着非常紧密的联系。从生物学上来看,这三个层级构成了神经元电活动的基本机制:
神经元细胞
Cell由细胞膜包围,膜上分布着各种离子通道Channel。离子通道
Channel控制离子Ion的进出。离子
Ion的流动会引起细胞Cell膜内外电位的变化,从而驱动神经元的电活动。
这些层级构成了神经元从微观机制到宏观动力学的完整建模路径。
核心功能#
braincell 的主要功能包括以下几个部分:
离子通道建模:支持通过模块化组件构建电生理精确的离子通道模型。
离子建模:支持通过模块化组件构建的离子模型。
神经元建模:提供基于 HH 模型的单房室和多房室神经元结构。
微分方程求解:支持基于JAX 的高性能微分方程求解器。
接下来,我们将深入探讨这些功能的使用方法和优化策略,帮助你从完整的神经元到精细的离子,全面掌握 braincell 的建模能力。
单房室神经元建模#
我们现在来讲解如何使用 braincell 对神经元进行建模工作。
以下是一个使用 braincell 对 HH 神经元建模的例子:
class HH(braincell.SingleCompartment):
def __init__(self, in_size):
super().__init__(in_size, C=Cm, solver='ind_exp_euler')
self.na = braincell.ion.SodiumFixed(in_size, E=50. * u.mV)
self.na.add(
INa=braincell.channel.INa_TM1991(in_size, g_max=(100. * u.mS * u.cm **-2) * area, V_sh=-63. * u.mV)
)
self.k = braincell.ion.PotassiumFixed(in_size, E=-90 * u.mV)
self.k.add(
IK=braincell.channel.IK_TM1991(in_size, g_max=(30. * u.mS * u.cm** -2) * area, V_sh=-63. * u.mV)
)
self.IL = braincell.channel.IL(
in_size,
E=-60. * u.mV,
g_max=(5. * u.nS * u.cm **-2) * area
)
我们建立的 HH 神经元模型继承自 SingleCompartment ,是一个单房室神经元。
而 SingleCompartment 是所有单房室神经元的基类,继承自 HHTypedNeuron 。
我们通过 HHTypedNeuron 对单房室神经元 SingleCompartment 和多房室神经元 MultiCompartment 进行建模。
SingleCompartment 中内置了有关膜电位的接口,同时支持接入多种 Channel 。
如其中的 INa_TM1991 、 IK_TM1991 以及 IL 都是通道 Channel 的具体子类。
以 INa_TM1991 为例,它继承自钠离子通道的基类 SodiumChannel ,并继承了相关的接口。
从本例能看出,使用 braincell 对具体的神经元进行建模,我们只需要对 Cell 、 Channel 、 Ion 三个层级的相关类进行引入组合即可。
在 braincell 中,这三个层级内部的继承关系很简单。
神经元 Cell 调控了各种离子 Ion 的流动,而离子 Ion 则通过离子通道 Channel 进行控制。
在上述HH神经元模型中,
神经元具有钠离子(实现为
SodiumFixed)、钾离子(实现为PotassiumFixed)。钠离子决定了钠离子通道
INa_TM1991的行为钾离子决定了钾离子通道
IK_TM1991的行为同时,
IL是一个漏电流通道,与任何离子无关。
可以看出,这种设计使得神经元模型的构建既灵活又模块化,便于扩展和修改。
神经网络建模#
基于BrainCell的单神经元建模的基础上,我们可以进一步构建神经网络模型,与BrainState的神经网络建模能力无缝集成。
接下来回到给出的例子,我们可以利用搭建的 HH 神经元网络模型进行一些实际工作。比如建立一个 E-I 网络:
V_th = -20. * u.mV
area = 20000 * u.um ** 2
area = area.in_unit(u.cm ** 2)
Cm = (1 * u.uF * u.cm ** -2) * area # Membrane Capacitance [pF]
class EINet(brainstate.nn.Module):
def __init__(self):
super().__init__()
self.n_exc = 3200
self.n_inh = 800
self.num = self.n_exc + self.n_inh
self.N = HH(self.num)
self.E = brainpy.state.AlignPostProj(
comm=brainstate.nn.EventFixedProb(self.n_exc, self.num, conn_num=0.02, conn_weight=6. * u.nS),
syn=brainpy.state.Expon(self.num, tau=5. * u.ms),
out=brainpy.state.COBA(E=0. * u.mV),
post=self.N
)
self.I = brainpy.state.AlignPostProj(
comm=brainstate.nn.EventFixedProb(self.n_inh, self.num, conn_num=0.02, conn_weight=67. * u.nS),
syn=brainpy.state.Expon(self.num, tau=10. * u.ms),
out=brainpy.state.COBA(E=-80. * u.mV),
post=self.N
)
def update(self, t):
with brainstate.environ.context(t=t):
spk = self.N.spike.value
self.E(spk[:self.n_exc])
self.I(spk[self.n_exc:])
spk = self.N(0. * u.nA)
return spk
# network
net = EINet()
_ = brainstate.nn.init_all_states(net)
D:\Document\PyCharm\Project\braincell(collaborator)\.venv\Lib\site-packages\braintools\surrogate.py:72: UserWarning: Explicitly requested dtype float64 requested in asarray is not available, and will be truncated to dtype float32. To enable more dtypes, set the jax_enable_x64 configuration option or the JAX_ENABLE_X64 shell environment variable. See https://github.com/jax-ml/jax#current-gotchas for more.
z = jnp.asarray(x >= 0, dtype=x.dtype)
# simulation
with brainstate.environ.context(dt=0.1 * u.ms):
times = u.math.arange(0. * u.ms, 100. * u.ms, brainstate.environ.get_dt())
spikes = brainstate.transform.for_loop(net.update, times, pbar=brainstate.transform.ProgressBar(10))
Running for 1,000 iterations: 100%|██████████| 1000/1000 [00:00<00:00, 8017.23it/s]
# visualization
t_indices, n_indices = u.math.where(spikes)
plt.scatter(times[t_indices], n_indices, s=1)
plt.xlabel('Time (ms)')
plt.ylabel('Neuron index')
plt.show()
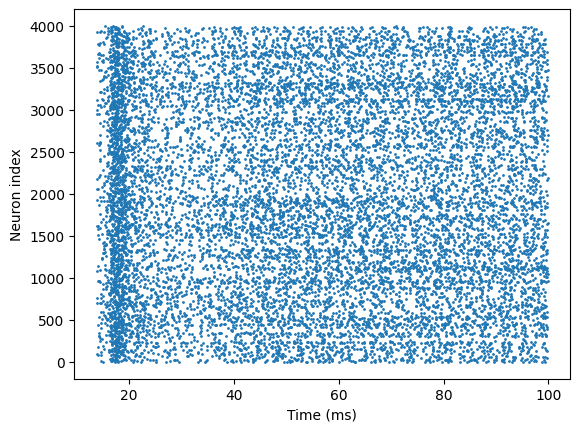
这样,我们就利用 braincell 对 HH 模型进行了建模,并实现了一个完整的 E-I 网络!
